Chapter 6: 마이크로바이옴–피부 상호작용 모델링과 디지털 트윈
왜 이 챕터인가
(Chapter 5)가 "단백질 한 개 × 대사체 한 개"의 결합을 예측하는 일이었다면, 이번 챕터는 다른 산수다 — 수십 종의 미생물 × 수십 종의 숙주 세포 × 시간이라는 다체 문제(many-body problem). 화장품 R&D에서 부딪치는 실제 질문은 거의 다 이쪽이다. "이 균주를 발라 두면 한 달 뒤 C. acnes–S. epidermidis 비율이 어떻게 변하는가", "L. ferment 발효물이 피부장벽 회복에 기여하는 경로의 어느 노드에 작용하는가", "동일한 활성 펩타이드가 지성 피부와 건성 피부에서 다른 결과를 내는 이유는 무엇인가" — 모두 두 분자 사이의 docking 점수로는 답이 안 된다. 군집 수준 동역학(community-level dynamics)을 모델링해야 한다.
이 챕터는 그 모델링이 2026년 현재 어디까지 와 있는지를 지도화한다. 그래프 신경망(graph neural network, GNN), 기계적 동역학 모델(Lotka–Volterra, agent-based, ODE), 멀티오믹스 통합, 그리고 산업이 "디지털 트윈(digital twin)"이라고 부르는 컨셉이 어떻게 연결되는지. 동시에 단단히 강조해야 할 한 가지: 2026년 5월 현재, ESM3 규모의 피부 마이크로바이옴 foundation model은 존재하지 않는다. critical-analyst가 이 책의 Gap 2로 지적한 빈 자리이고, 이 챕터의 가장 중요한 메시지 중 하나다.
이 챕터의 정량적 핵심 3가지 1. 군집 모델링의 두 가지 흐름 — 데이터 기반 GNN(SIMBA-GNN, [24])과 기계적 ODE/agent-based 모델(Lotka–Volterra 확장, in vitro microecology). 둘은 서로 보완한다. 2. 데이터 비대칭 — Unilever 30,000 샘플 사내 코호트, COSMAX FACE-LINK 950명 ([19])는 foundation model 학습이 기술적으로 가능한 규모지만, 어디도 외부 공개를 한 적이 없다. 3. 디지털 트윈의 정의 격차 — L'Oréal Skin Genius, Unilever virtual cohorts(2,500명), POND's Skin Institute analyzer ([23])는 상업적으로 트윈을 주장한다. 방법론적으로 검증된 트윈(예측 + 측정 + 오차 정량 + 외부 일반화)은 아직 동료 심사 채널에 없다 ([7]).
6.1 군집 문제 — pairwise로는 닿지 않는 영역
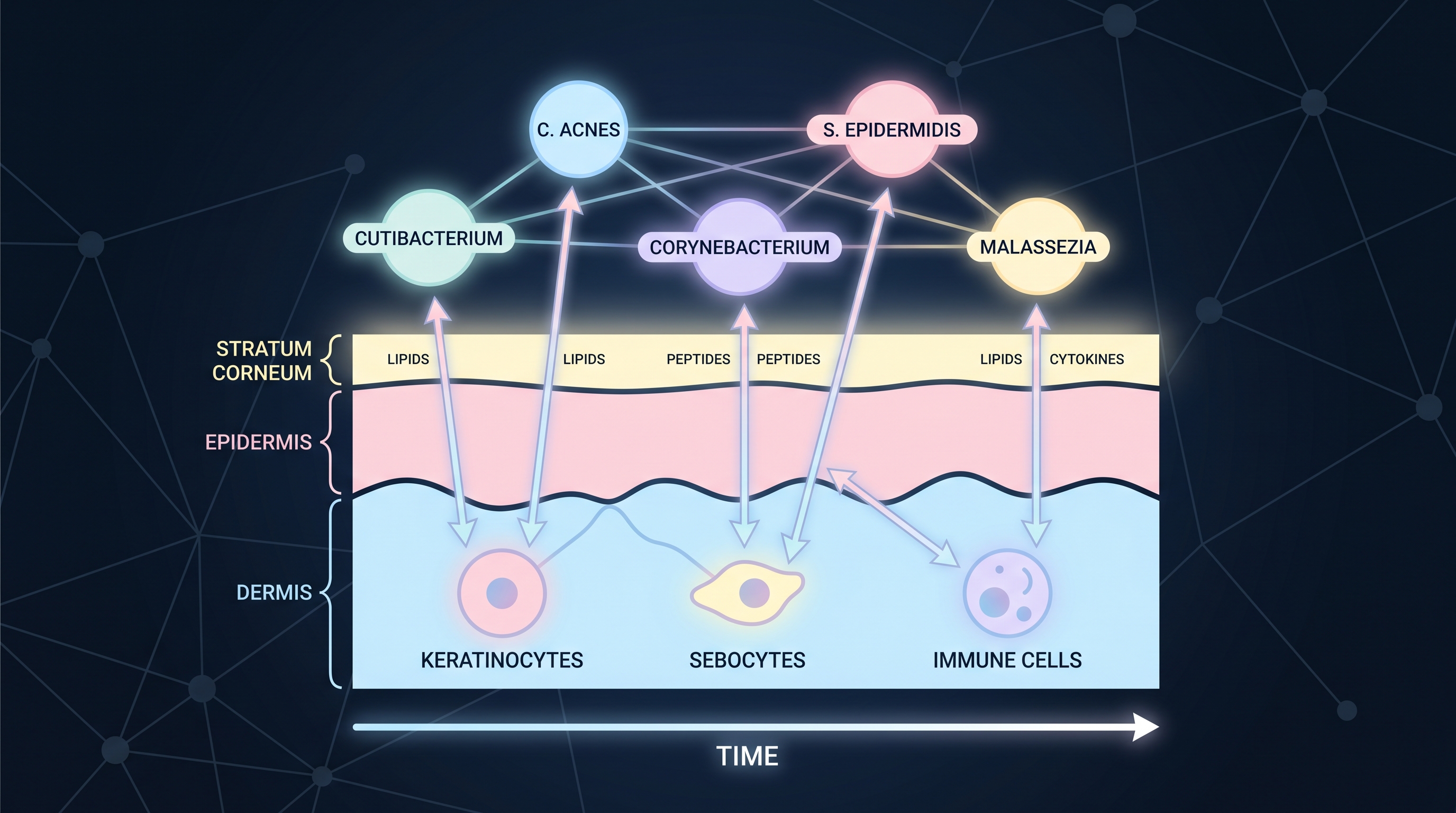
(Chapter 5)가 다룬 단백질-리간드 docking 모델의 가장 큰 가정은 2개체 평형(two-body equilibrium)이다. 두 분자 사이의 결합 친화도가 정해지면 효능을 추정한다. 마이크로바이옴은 이 가정이 거의 통하지 않는다.
피부 사이트 한 곳에서만 봐도 Cutibacterium acnes가 단독으로 작용하는 시나리오는 드물다 — S. epidermidis가 인근에서 epifadin류 폴리엔 펩타이드를 분비하고 [13], 동시에 Malassezia가 지질 가수분해로 유리지방산을 방출하며, 그 유리지방산이 C. acnes의 비정상 증식을 유도하고, 숙주 keratinocyte가 NF-κB·AHR을 통해 반응한다 ([3]). [11]는 건강한 피부장벽에서는 commensal로 분류되던 S. epidermidis가 손상된 장벽 위에서는 오히려 염증을 악화한다는 점을 보여줘, "균주-효능"이 균주의 정체성이 아니라 맥락에 달려 있음을 명시했다. (Chapter 2)에서 정리한 strain-level 동역학 ([16])과 합쳐 보면, 그림은 이렇다 — 같은 종이라도 strain이 다르고, 같은 strain이라도 이웃 군집과 숙주 상태에 따라 다른 일을 한다.
이런 다체 시스템을 pairwise 예측의 합으로 환원하는 시도는 두 가지 이유로 실패한다. 첫째, 비선형 상호작용 — 세 균이 모이면 두 균 짝의 합과 다른 대사가 일어난다. 둘째, 시간 의존성 — C. acnes가 IA1형에서 II형으로 천이하는 데 수 주가 걸리고, 그 사이 S. epidermidis는 변화 없이 머문다 ([21]). 단일 시점 데이터에서 도출한 예측은 다음 시점에서 깨진다.
군집 모델링의 출발점은 네트워크 표현이다. 종(또는 strain)을 노드, 상호작용을 엣지로 두고, 엣지의 무게를 학습하거나(데이터 기반) 미분방정식으로 결정한다(기계적). 그 위에 숙주 세포 노드를 얹으면 host–microbe interaction network가 되고, 그 위에 다시 시간 축을 얹으면 dynamics 모델이 된다. 이 챕터는 그 stack을 위에서 아래로 본다.
6.2 그래프 신경망 — 데이터로 엣지를 학습한다
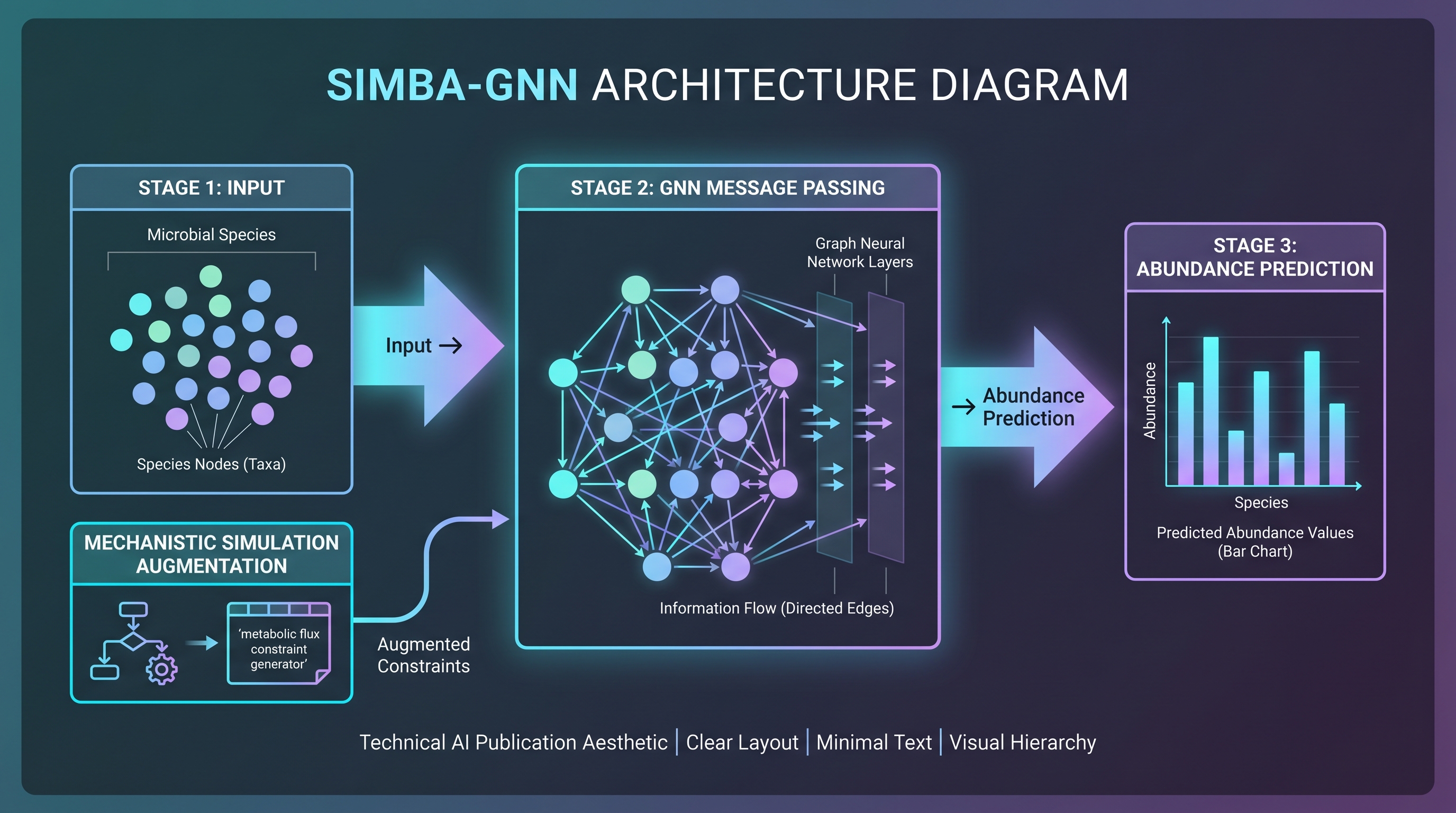
미생물 군집을 그래프로 학습하는 가장 자연스러운 도구는 GNN이다. 노드 임베딩이 message passing을 통해 이웃의 정보를 흡수하고, 그 결과로 community-level 표현을 만들어 downstream 분류기·회귀기에 넘긴다.
SIMBA-GNN [24]가 npj Systems Biology and Applications에 발표한 모델은 이 흐름의 2025년 산물이다. SIMBA는 Simulation-augmented Microbiome Abundance GNN의 약자로, 데이터만으로 학습하는 순수 GNN의 가장 큰 약점 — 학습 분포 밖의 perturbation(예: 새 활성 성분 도포)에서의 일반화 — 를 ODE 기반 mechanistic 시뮬레이션 데이터를 보조 학습 신호로 섞어 보완하는 hybrid 구조다. 모델 입력은 16S 또는 shotgun 기반 상대 풍부도 벡터, 출력은 임의의 시점에서의 풍부도 예측. 검증은 주로 gut 코호트에서 이루어졌지만, 저자들은 "데이터 도메인 자체를 바꾸지 않고 피부 코호트로 확장 가능"이라 명시했다. 피부 적용 readout은 아직 없다.
GNN을 미생물 도메인에 가져온 더 이른 흐름은 두 갈래로 정리된다. 첫째, DeepMicro·MetaPhlAn 후속 임베딩 학습 — taxonomic 프로파일에서 phenotype을 예측하는 분류기. 둘째, community-level metabolite production 예측 — 종 그래프에서 message passing으로 community가 생산하는 대사체를 예측. [12]가 정리한 AI-microbiome 200+ 논문 메타리뷰는 GNN/Transformer가 마이크로바이옴에서 빠르게 채택되고 있다고 보고하지만, "피부 적용은 장에 비해 매우 제한적"이라는 단서를 단다. [25] 종설은 같은 메시지를 더 강하게 — "gut-only focus; skin equivalents lag" — 표현한다.
여기에 인접 도메인의 시사 하나가 있다. [14]는 Science Advances에 cell-cell communication network 기반의 interpretable ML을 이용해 암 환자의 면역 체크포인트 억제제 반응을 예측한 사례를 발표했다 — 마이크로바이옴이 아닌 종양 면역 도메인이지만, "노드 간 message passing + 해석 가능성"이라는 골격이 동일하다. 화장품 마이크로바이옴 도메인의 다음 발걸음 중 하나가 이 형태일 가능성이 높다 — 균종-숙주 세포 cross-talk 네트워크를 GNN으로 학습한 뒤, SHAP 또는 attention 분석으로 어떤 노드가 phenotype을 끌고 가는지를 해석 가능한 형태로 산출.
GNN의 산업적 가치는 결국 predict-validate 루프의 단축이다. 균주 조합 10,000개의 시너지를 예측하려고 wet-lab assay를 모두 돌리는 대신, GNN으로 top 50을 추리고 그것만 검증한다. (Chapter 4)에서 다룬 endpoint별 ML triage와 같은 논리지만, 입력이 분자가 아니라 군집이라는 점이 다르다.
6.3 기계적 모델 — 미분방정식이 여전히 답하는 것
GNN이 데이터에서 엣지를 학습한다면, 기계적 모델은 엣지를 가정한다. 가장 오래된 도구는 Lotka–Volterra 일반화 모델(gLV) — 종 풍부도의 시간 변화를 종간 상호작용 계수 행렬로 표현하는 ODE 시스템이다. 화장품 도메인에서는 직접적 readout이 드물지만, gut 마이크로바이옴 연구에서는 표준 도구로 자리잡았고 ([12], [25]), SIMBA-GNN의 mechanistic augmentation 자체가 gLV에 가까운 simulator를 쓴다.
Agent-based skin model은 다른 추상화 수준이다. 각 미생물을 격자 위의 에이전트로 두고, 영양·산소·pH·항생물질의 국소 농도를 ODE로 풀면서 에이전트의 성장·이동·죽음을 시뮬레이션한다. [28]가 Biotechnology Journal에 정리한 organoid-based skin and lung biofilm 미니 리뷰는 이 흐름의 in vitro 대응물 — 3D 피부 organoid 위에 다균 biofilm을 키워 실제 데이터를 채집하는 인프라 — 가 2024–2025년 사이에 빠르게 표준화되고 있음을 보여준다. [18]가 Nature Communications에 발표한 micro-ecology in vitro 모델은 더 야심차다 — 인간 피부 마이크로바이옴의 다균 상호작용을 in vitro에서 재현하면서 실험 변수를 통제할 수 있는 platform — 이는 mechanistic 모델의 파라미터를 fit할 ground truth를 제공한다는 점에서 GNN-only 접근보다 정량적으로 강력하다.
Diffusion ODE — 대사체의 시공간 분포 — 도 화장품 도메인에서 점차 중요해진다. 한 활성 성분이 피부 stratum corneum 위에서 시간에 따라 어떻게 분포하고, 그 농도가 미생물 군집에 미치는 국소 영향을 예측하려면 — Fickian diffusion + 미생물 흡수 항을 결합한 PDE를 풀어야 한다. 이 모델링은 (Chapter 8)에서 다룰 AI formulation 설계의 입력 중 하나가 된다.
기계적 모델의 가장 큰 강점은 외삽 가능성이다. 학습 분포 밖의 perturbation에 대해서도 — 모델이 옳다면 — 합리적 예측을 낸다. 가장 큰 약점은 파라미터 결정이다. gLV의 상호작용 계수 행렬은 종 수의 제곱에 비례해 커지며, 화장품 피부 마이크로바이옴에서 모든 짝의 계수를 wet-lab으로 측정하는 것은 비현실적이다. SIMBA-GNN 같은 hybrid 접근이 자연스러운 이유 — 데이터로 계수를 학습하고 mechanism으로 정규화한다.
6.4 멀티오믹스 통합 — 16S + 대사체 + 전사체
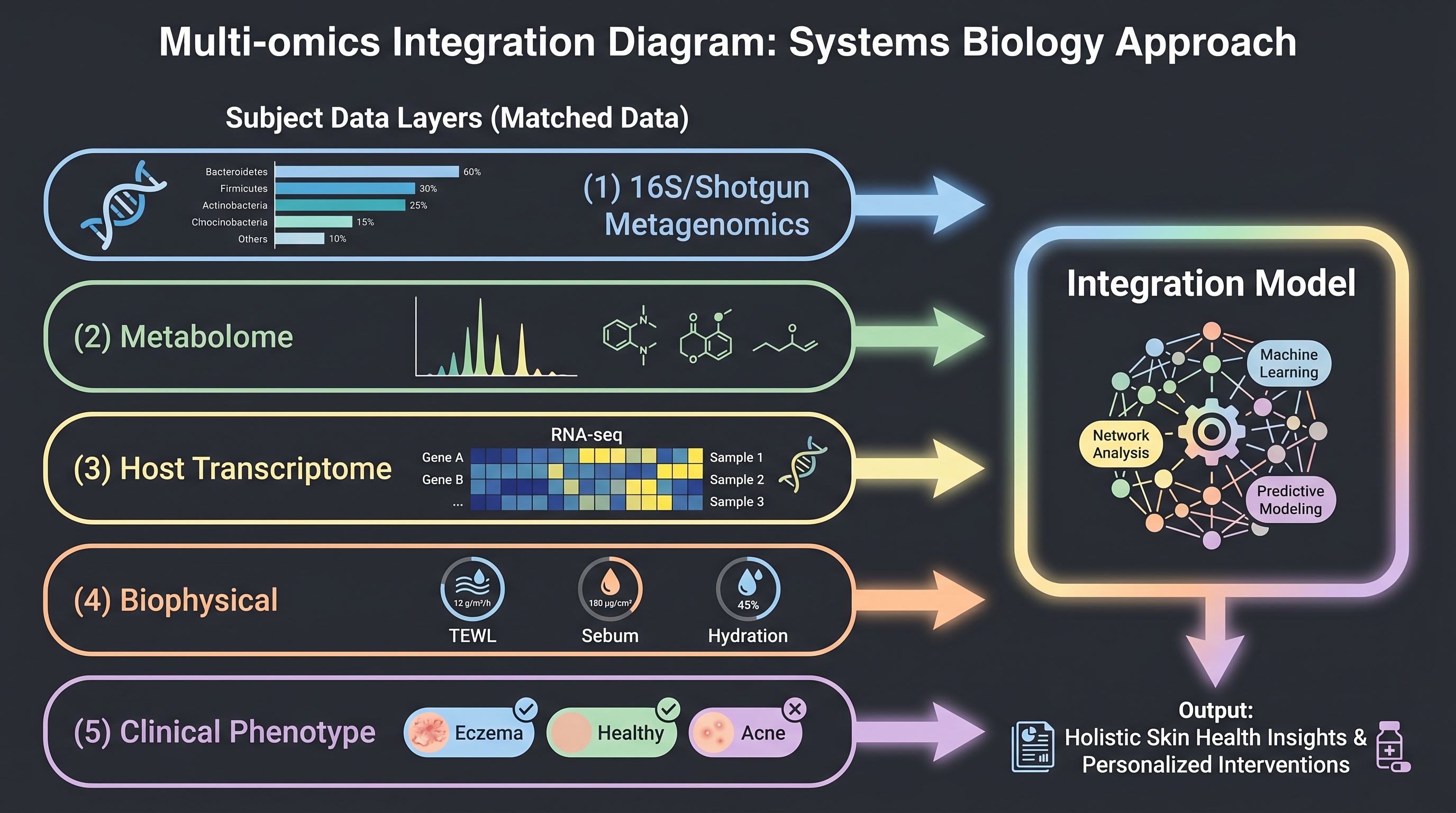
군집 모델링의 입력은 한 종류가 아니다. 같은 개인에서 같은 시점에 얻은 16S (또는 shotgun) + metabolome + skin transcriptome이 매칭될 때 모델이 가장 강력해진다. 그 매칭이 이뤄진 reference 코호트는 의외로 적다.
- HMP / iHSMGC — taxonomic profile은 잘 정리되어 있지만 metabolome·transcriptome은 부재. iHSMGC [15]는 10.94M 유전자 카탈로그를 제공하며 그 중 ~45%가 HMP에 보이지 않던 신규로, 인종·지역 일반화의 한계를 정량적으로 보여준 자산이다.
- Unilever 30K — [26]가 공개한 자체 추산. 30,000 샘플, 50억 데이터 포인트로 16S + biophysical + (일부) metabolomics가 매칭되어 있다고 알려졌지만, 외부 접근 불가.
- COSMAX × Dankook FACE-LINK — [19]가 Frontiers in Cellular and Infection Microbiology에 발표한 950명 한국인 cohort. 16S + biophysical(수분, TEWL, 멜라닌, 홍반)이 매칭되어 있다. 한국 산업이 외부 공개한 가장 큰 매칭 cohort.
- L'Oréal 사내 — Modjoul·Modiface 디바이스 데이터 + 2023년 Lactobio 인수로 흡수한 ~10,000균주 collection. Multi-omics 통합 수준은 비공개.
- iHSMGC + ZOE PREDICT — 직접 매칭은 아니지만, [2] PREDICT 1 코호트(1,098명, gut microbiome + 식이 + 대사 phenotype)는 (Chapter 11)에서 다룰 skin-gut axis 모델링의 reference로 활용된다.
이 데이터 지형이 곧 시퀀싱 깊이의 의미다 — (Chapter 3)에서 다룬 16S·shotgun·long-read의 trade-off는 모델의 입력 차원에 직접 매핑된다. 16S만 있으면 종 수준 풍부도 벡터, shotgun이면 기능 유전자(KO/EggNOG)까지 입력, metabolomics가 더해지면 대사체 vector, transcriptome이면 숙주 반응까지 — 입력 차원이 커질수록 모델이 잡을 수 있는 인과 가설이 늘어난다. 하지만 차원이 커질수록 공개 데이터는 줄어든다. [22]이 microbiome ML의 표준 함정으로 정리한 compositionality·high dimensionality·batch effect·leakage는 멀티오믹스 통합에서 더 심해진다 — 각 오믹스 layer가 자기의 batch effect를 갖고 들어오기 때문에.
이 맥락에서 [4]가 Nature에 발표한 skin autonomous antibody production 연구는 의미가 크다 — 피부 자체가 면역글로불린을 만들고 그것이 마이크로바이옴 구성을 조절한다는 발견은, 모델링 입력에 피부 면역 시그니처라는 새 차원이 추가되어야 함을 시사한다. (Chapter 9)의 임상 시뮬레이션에서 다시 호출될 결과다.
6.5 디지털 트윈 — 누가 무엇을 트윈이라 부르고 있는가
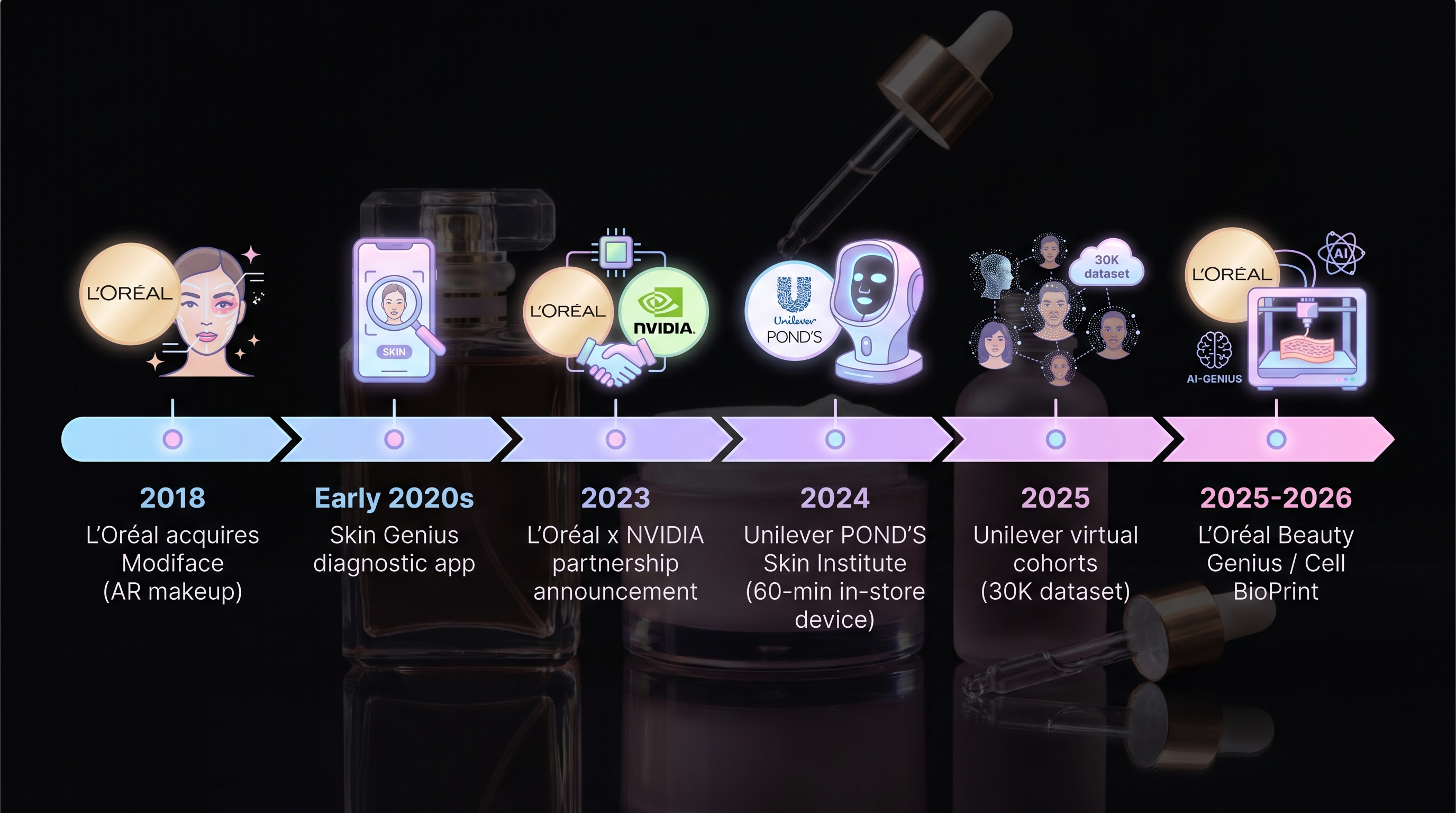
산업에서 "디지털 트윈(digital twin)"·"스킨 트윈(skin twin)"·"마이크로바이옴 트윈"은 2024년 이후 급격히 자주 등장하는 용어다. 정의가 매번 다르다는 점이 문제다. 이 챕터는 그 정의 격차를 명시한다.
기술적 정의(원형) — 디지털 트윈은 (1) 실제 시스템의 현재 상태를 데이터로 표현하고, (2) 그 시스템에 가할 perturbation에 대해 미래 상태를 예측하며, (3) 측정과 비교해 자기를 업데이트하는, 살아있는 모델이다. 제조업·항공·도시 인프라에서 이 정의는 안정적이다.
산업의 사용(화장품/마이크로바이옴) — 위 정의의 어느 부분만 가져다 쓰는 경우가 많다.
- L'Oréal Skin Genius / Beauty Genius / Cell BioPrint — [17]가 공개한 AI 진단 도구. 이미지·설문 입력에서 피부 상태와 제품 추천을 산출. 외부 검증 readout은 없고, [7] PRISMA 종설은 "digital-twin 주장이 상업적 데모에 의존, 동료 심사 검증 부재"라고 명시했다.
- Unilever virtual cohorts — [26]가 SXSW에서 공개한 2,500명 시뮬레이션 코호트. consumer insight를 60% 가속하고, formulation cycle을 5~6에서 1~2로, claims development를 75% 가속했다고 보고. operational KPI는 보고됐지만 일반화 오차는 보고되지 않았다 ([27]).
- POND's Skin Institute analyzer — [23]가 Unilever 발표로 공개한 60분 in-store 디바이스. 마이크로바이옴 스왑 → 제품 추천 워크플로우. 실시간 의사결정 도구로서의 성능 readout은 비공개.
- COSMAX × Bertis 피부 프로테옴 — [5]가 공개한 한국 산업의 proteome 기반 노화 모델 시도. "트윈"이라는 용어를 명시적으로 쓰지는 않지만, individual-level proteomic 시그니처에서 화장품 추천을 도출하는 구조는 같은 계보.
- Infant microbiome 디지털 트윈 — [9] U. Chicago 그룹이 PNAS / npj Biofilms에 발표한 사례. 유아 장 마이크로바이옴 트윈이며 피부가 아니지만, 트윈이라는 용어를 동료 심사 채널에서 가장 정직하게 정의한 사례 — 입력, 예측, ground truth, 일반화를 모두 명시.
이 목록에서 한 가지가 명확해진다 — 화장품 회사의 "디지털 트윈"은 마케팅적으로 트윈이지만 방법론적으로 트윈에 부족하다. [7]가 PRISMA 방법론으로 74편을 검토한 결과, AI 디자인 화장품 활성 성분의 외부 동료 심사 임상 readout이 0건이듯, 동료 심사된 디지털 트윈 외부 검증도 거의 없다. 이 챕터의 가장 솔직한 한 줄: 현재 산업이 "트윈"이라 부르는 대부분은 personalization layer가 붙은 추천 시스템이다 — 그 자체로 가치가 없는 것은 아니지만, 마이크로바이옴 동역학을 예측하고 검증하는 트윈이라 부르려면 더 많은 것이 필요하다.
6.6 The Foundation Model 격차 — Gap 2를 정면으로
critical-analyst가 이 챕터에 부여한 가장 무거운 메시지는 이것이다. 2026년 5월 현재, ESM3 규모의 피부 마이크로바이옴 foundation model은 존재하지 않는다.
비교 기준점이 명확하다. 단백질 도메인에서는 ESM3 [8]가 98B 파라미터 모델로 5억 년 진화 시뮬레이션을 학습했고, 7B는 오픈소스로 풀렸다. 그 위에 AlphaFold 2/3 [10]가 PDB·UniProt·AlphaFold DB를 reference 인프라로 만들었다. 단백질의 inflection이 공개 자산 + foundation model의 결합이었다면, 마이크로바이옴은 둘 다 부족하다.
마이크로바이옴 쪽에서 foundation model이라 부를 수 있는 후보는 다음 정도다. [12]가 200+ 논문을 종합한 결과 — 마이크로바이옴 AI에 적용된 Transformer/GNN/생성 모델이 빠르게 늘었지만 — 피부 적용은 "장에 비해 매우 제한적"이다. [6]가 2024년 SoTA로 꼽은 COMEBin은 metagenomic binning 모델이지 foundation model이 아니다. [25] 종설은 "gut-only focus; skin equivalents lag"라고 단언한다.
왜 비어 있는가. 이유는 단순하다.
- 데이터 corpus의 비공개성 — foundation model 학습에 필요한 규모(수만~수십만 개인의 매칭 멀티오믹스)는 산업 내부에 갇혀 있다. Unilever 30K, L'Oréal 사내, COSMAX FACE-LINK 950, BGI/iHSMGC — 가장 큰 자산들은 모두 사적이다 ([15], [19], [26]).
- 윤리·동의의 분절성 — 피부 마이크로바이옴 샘플링은 IRB 승인이 필요하고, 동의 범위가 표본마다 다르다. foundation model 학습용으로 cross-cohort merge하는 데 법적 장벽이 있다.
- 멀티모달성 — 단백질은 서열·구조라는 비교적 통일된 representation을 갖지만, 마이크로바이옴은 16S·shotgun·metabolome·transcriptome·biophysical·임상이 모두 다른 modality다. 통합 representation을 정의하는 것 자체가 미해결 문제다.
- 시간 차원 — 마이크로바이옴은 시간에 따라 변하는 dynamical system이지, 단백질처럼 평형 구조가 아니다. foundation model의 학습 목표가 어느 시점의 어떤 표현을 학습해야 하는지부터 합의가 부족하다.
foundation model이 만약 생긴다면 무엇을 풀어줄 것인가. 적어도 다음 셋: (a) zero-shot 군집 동역학 예측 — 학습되지 않은 perturbation(새 활성 성분)에 대해 군집 변화를 예측, (b) cross-cohort 일반화 — 한국 cohort에서 학습한 모델이 EU·미국 코호트에 안정적으로 외삽, (c) 멀티오믹스 stitching — 일부 modality만 있는 새 개인에 대해 누락 modality를 합리적으로 imputation. 어느 것도 현재 가능하지 않다.
해결 방향의 후보는 두 가지다. 데이터 cooperative — 산업·학계가 federated learning이나 differential privacy를 써서 자체 데이터를 공유하지 않고 모델을 함께 학습. iHSMGC가 BGI 주도로 만들어졌듯 한국·중국·EU 산업이 cooperative를 형성하는 시나리오. 공개 reference 코호트 확장 — HMP/iHSMGC를 잇는 차세대 reference에 multi-omics를 매칭해 공개. (Chapter 12)가 청사진 차원에서 이 두 후보의 실현 가능성을 본격 분석한다.
이 격차는 화장품 마이크로바이옴 AI의 천장이다. 격차가 닫히지 않으면, 모든 task-specific 모델은 학습 corpus 크기에 묶여 성능이 한계 짓는다 — Gap 2의 가장 직접적 의미다.
6.7 한계와 위험
군집 모델링과 트윈이 약속하는 가치만큼 위험도 명시되어야 한다.
과적합과 분포 외 실패 — Unilever virtual cohorts 2,500명은 어떻게 시뮬레이션된 모집단인지가 외부에서 검증된 적이 없다. 학습 코호트에서 5점짜리 모델이 신규 모집단에서 2점이 되는 시나리오 — 영상의학·약물 효능 예측에서 반복적으로 관찰된 — 가 마이크로바이옴에서 반복될 가능성은 낮지 않다. [7]가 "geographic diversity 제한, darker phototype 과소대표"를 PRISMA 종설의 명시적 한계로 적었듯, 인종·연령·환경 편향은 트윈의 일반화에 직접 영향을 미친다.
마케팅과 과학의 간극 — 산업 발표 KPI(60% 가속, 75% 가속)와 동료 심사된 검증 사이의 간극은 (Chapter 4)에서 다룬 Gap 15와 같은 줄기다. 트윈 주장이 마케팅 무기로 사용될 때, 소비자·R&D 결정자는 무엇이 검증되었고 무엇이 시뮬레이션인지를 구분할 도구를 갖지 못한다. 이 책의 직접적 기여 중 하나는 그 구분의 vocabulary를 제공하는 것이다.
프라이버시와 개인화 — 마이크로바이옴은 부분적으로 지문이다 ([20]). 트윈이 individual-level로 정밀해질수록 개인 식별·재식별 위험도 커진다. 화장품 회사가 트윈을 운영할 때 GDPR·KISA 등의 개인정보 규제와의 마찰면이 분명해진다 — 활용 사례별 동의 범위, 모델에서의 개인 정보 inversion 위험.
모델 드리프트 — 마이크로바이옴은 계절·식습관·기후·연령에 따라 천천히 변한다 ([21]가 보고한 1–2년 안정성은 부위마다 다르다). 트윈이 2024년에 학습된 그대로 2027년에 의사결정을 한다면, 그 사이의 drift가 예측 오차로 쌓인다. continual learning과 재학습 주기가 트윈 운영의 일부가 되어야 한다 — 이는 단순한 모델 배포가 아니라 시스템 운영 문제다.
이 한계들은 model engineering 문제가 아니라 데이터·거버넌스·검증 문제다. 모델 아키텍처를 바꿔서는 닫히지 않는다. (Chapter 12)가 그 거버넌스 청사진을 본격적으로 다룬다.
6.8 Open Questions
- Foundation model의 최소 데이터 규모 — 피부 마이크로바이옴 foundation model이 의미 있는 zero-shot 일반화를 보이려면 매칭 멀티오믹스 cohort가 몇 명 필요한가? 단백질(UniProt 250M+) 대비 추정조차 어렵다. 학습 곡선의 정점이 50K에서 평탄해진다면 산업 cooperative가 합리적이지만, 1M 이상이 필요하다면 어떤 cooperative도 닿지 못한다.
- 트윈의 validation 기준 — "이 모델은 트윈이다"를 판정할 최소 조건은 무엇인가? (a) prospective 예측, (b) ground-truth 측정, (c) 오차 정량, (d) 외부 모집단 일반화 — 이 네 가지가 [9]의 골격이지만, 화장품 도메인의 endpoint(예: 8주 후 hydration 점수)에 맞게 어떻게 구체화할지는 합의가 없다.
- 장기 안정성 — 트윈이 학습된 시점의 마이크로바이옴 baseline이 사용자의 5년 후 baseline과 얼마나 다른가? [21]의 1–2년 안정성 데이터는 화장품 출시 cycle(보통 5년)에 충분하지 않을 수 있다 — drift 모니터링의 산업 표준이 부재.
- 개체 vs 군집 트윈 — "skin twin"이 개인의 트윈인지, 인구 segment의 트윈인지가 종종 흐려진다. Unilever virtual cohorts 2,500명은 segment 트윈에 가깝고, L'Oréal Skin Genius는 개인 트윈을 주장한다. 두 접근은 데이터·검증·법적 책임이 다르다 — 명료한 구분이 산업 차원에서 부재.
- 합성 데이터의 역할 — virtual cohort의 시뮬레이션 샘플이 실제 분포를 얼마나 잘 대표하는가? mechanistic ODE 기반 augmentation([24])이 학습 신호로 가치 있지만, 검증 데이터로 쓰는 것은 별개의 위험이다. 학습/검증의 경계가 산업 KPI에서 종종 흐려진다.
참고문헌
- Abramson, J., Adler, J., Dunger, J. et al. (2024). Accurate structure prediction of biomolecular interactions with AlphaFold 3. Nature 630, 493–500.
- Asnicar, F., Berry, S. E., Valdes, A. M. et al. (2021). Microbiome connections with host metabolism and habitual diet from 1,098 deeply phenotyped individuals. Nature Medicine 27, 321–332.
- Belkaid, Y. and Segre, J. A. (2014). Dialogue between skin microbiota and immunity. Science 346(6212), 954–959. [Belkaid et al., 2014]
- Belkaid, Y. et al. (2024). Skin autonomous antibody production regulates host-microbiota interactions. Nature, December 2024. [Belkaid et al., 2024]
- COSMAX × Bertis (2024). COSMAX × Bertis skin proteome anti-aging partnership. The Monodist, 2024–2025. [COSMAX × Bertis, 2024]
- Deep learning microbiome review — Wang, T., Yang, L. et al. (2024). Deep learning in microbiome analysis: a comprehensive review of neural network models. Frontiers in Microbiology 15:1516667. [Deep learning microbiome review, 2024]
- Haykal, D., Flament, F., Amar, D. et al. (2025). Cosmetogenomics unveiled: a systematic review of AI, genomics, and the future of personalized skincare. Frontiers in Artificial Intelligence 8:1660356.
- Hayes, T., Rao, R., Akin, H. et al. (2025). Simulating 500 million years of evolution with a language model (ESM3). Science, 2025.
- Infant microbiome digital twin authors — U. Chicago group (2024). A digital twin of the infant microbiome to predict neurodevelopmental deficits. PNAS / npj Biofilms, 2024. [Infant microbiome digital twin, 2024]
- Jumper, J., Evans, R., Pritzel, A. et al. (2021). Highly accurate protein structure prediction with AlphaFold. Nature 596, 583–589.
- Khadka, V. D. et al. (2024). Commensal skin bacteria exacerbate inflammation on damaged skin barriers. Journal of Investigative Dermatology, 2024. [Khadka et al., 2024]
- Wang, X.-W., Wang, T., Liu, Y.-Y. (2024). Artificial Intelligence for Microbiology and Microbiome Research. arXiv preprint 2411.01098. [Wang et al., 2024]
- Krismer, B., Peschel, A. et al. (2024). Commensal production of broad-spectrum antimicrobial peptide polyene eliminates nasal S. aureus (epifadin). Nature Microbiology, 2024.
- Lee, J., Kim, D., Kong, J. et al. (2024). Cell-cell communication network-based interpretable machine learning predicts cancer patient response to immune checkpoint inhibitors. Science Advances 10:eadj0785.
- Li, Z., Xia, J., Jiang, L. et al. (2021). Characterization of the human skin resistome and identification of two microbiota cutotypes (iHSMGC catalog). Microbiome 9:47.
- Li, Z., Xia, J., Wang, J. (2025). Unveiling strain-level dynamics in the human skin microbiome (Preview of Jacob et al.)00097-6). Cell Host & Microbe 33(5):615–617.
- L'Oréal R&I Press (2024). L'Oréal Beauty Tech leadership at VivaTech 2024 — AI Skin Genius, Modiface, microbiome direction. L'Oréal press, May 2024. [L'Oréal VivaTech, 2024]
- Microecology in vitro authors (2025). Microecology in vitro model replicates the human skin microbiome interactions. Nature Communications, 2025. [Microecology in vitro, 2025]
- Mun, S., Jo, H., Heo, Y. M. et al. (2025). Skin microbiome-biophysical association: a first integrative approach to classifying Korean skin types and aging groups (FACE-LINK). Frontiers in Cellular and Infection Microbiology 15:1561590.
- Oh, J., Byrd, A. L., Deming, C. et al. (2014). Biogeography and individuality shape function in the human skin metagenome. Nature 514, 59–64. [Oh et al., 2014]
- Oh, J., Byrd, A. L., Park, M. et al. (2016). Temporal Stability of the Human Skin Microbiome30399-3). Cell 165(4), 854–866. [Oh et al., 2016]
- Papoutsoglou, G., Tarazona, S., Lopes, M. B. et al. (2023). Machine learning approaches in microbiome research: challenges and best practices. Frontiers in Microbiology 14:1261889.
- POND's / Unilever (2024). POND's Skin Institute microbiome analyzer — 60-minute in-store consumer device. Unilever press, May 2024. [POND's, 2024]
- SIMBA-GNN authors (2025). SIMBA-GNN: Simulation-augmented Microbiome Abundance GNN. npj Systems Biology and Applications, 2025. [SIMBA-GNN, 2025]
- Transformer-microbiome authors (2024). Transformer Models, Graph Networks, and Generative AI in Gut Microbiome Research. Bioengineering 13(2):144. [Transformermicrobiome, 2024]
- Unilever Beauty & Wellbeing R&D (2025). How Unilever's pioneering skin microbiome research is shaping product innovation. Unilever news; SXSW 2025 + R&D page coverage. [Unilever, 2025]
- Unilever (2026). Unilever 2026 forward outlook — AI transforming Beauty & Wellbeing innovation. Unilever news, 2026. [Unilever, 2026]
- Verma, P. et al. (2025). Organoid-Based Skin and Lung Biofilm Models — Mini Review. Biotechnology Journal, 2025. [Verma et al., 2025]